怎样使用Clustal进行多序列比对,相信很多没有经验的人对此束手无策,为此本文总结了问题出现的原因和解决方法,通过这篇文章希望你能解决这个问题。
多序列比对在保守区域鉴定,系统发育分析,motif识别等多个领域发挥重要作用,是生物信息数据分析必备的基础技能之一。Clustal是一款经典的多序列比对工具,支持DNA, RNA, 蛋白质的比对。
clustal 有两个版本可用,之前的版本同时提供了GUI和命令行两种工具,GUI版的叫做ClustalX, 命令行版叫做ClustalW; 最新版本叫做Omega, 只提供了命令行版。

最新本的omega比对准确度更高,而且速度更快,适合几千条规模的多序列比对,该软件目前只提供了命令行版本。在官网上,提供了源代码和编译好的二进制文件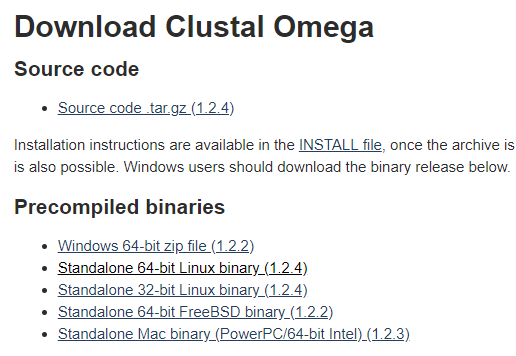
通常情况下,直接下载对应的二进制可执行文件就行了。软件的基本用法如下:
clustalo -i seq.fasta > align.fa-i指定输入的序列文件,默认输出结果打印在屏幕上,可以重定向到指定文件中。该软件支持多种格式的输出
fasta
clustal
msf
phylip
selex
stockholm
vienna
默认输出格式为fasta, 可以通过--outfmt参数指定输出文件的格式。多序列比对不同于Blast的地方在于,Blast是局部比对,而多序列比对是全局比对。全局比对意味着需要将输入序列对齐到同一个水平来比对,一般是通过在输入序列中插入碱基的方式来使序列对齐,示意如下
>ENA|CAA23748|CAA23748.1 Homo sapiens (human) alpha globin
ATGGTGCTGTCTCCTG----CCGACAAGACCAACGTCAAGGCCGCCTGGGGTAAGGTCGG
CGCGCACGCTGGCGAGTATGGTGCGGAGGCCCTGGAGAGGATGTTCCTGTCCTTCCCCAC
CACCAAGACCTACTTCCCGCACTTC---GACCTGAGCCACGGCTCTGCCCAAGTTAAGGG
CCACGGCAAGAAGGTGGCCGACGCGCTGACCAACGCCGTGGCGCACGTGGACGACATGCC
CAACGCGCTGTCCGCCCTGAGCGACCTGCACGCGCACAAGCTTCGGGTGGACCCGGTCAA
CTTCAAGCTCCTAAGCCACTGCCTGCTGGTGACCCTGGCCGCCCACCTCCCCGCCGAGTT
CACCCCTGCGGTGCACGCTTCCCTGGACAAGTT---CCTGGCTTCTGTGAGCACCGTGCT
GACCTCCAAATACCGTTAA
>ENA|CAA24095|CAA24095.1 Mus musculus (house mouse) alpha-globin
ATGGTGCTCTCTGGGGAAGACAAAAG----CAACATCAAGGCTGCCTGGGGGAAGATTGG
TGGCCATGGTGCTGAATATGGAGCTGAAGCCCTGGAAAGGATGTTTGCTAGCTTCCCCAC
CACCAAGACCTACTTTCCTCACTTTGATGT---AAGCCACGGCTCTGCCCAGGTCAAGGG
TCACGGCAAGAAGGTCGCCGATGCGCTGGCCAGTGCTGCAGGCCACCTCGATGACCTGCC
CGGTGCCTTGTCTGCTCTGAGCGACCTGCATGCCCACAAGCTGCGTGTGGATCCCGTCAA
CTTCAAGCTCCTGAGCCACTGCCTGCTGGTGACCTTGGCTAGCCACCACCCTGCCGATTT
CACCCCCGCGGTACATGCCTCTCTGGACAAATT---CCTTGCCTCTGTGAGCACCGTGCT
GACCTCCAAGTACCGTTAA
>ENA|BAA20512|BAA20512.1 Cyprinus carpio (common carp) alpha-globin
ATGAGTCTCTCTGATAAGGACAAGGCTG----CTGTGAAAGCCCTATGGGCTAAGATCAG
CCCCAAAGCCGATGATATCGGCGCTGAAGCTCTCGGCAGAATGCTGACCGTCTACCCTCA
GACCAAGACCTACTTCGCTCACTGGGATGACCTGAGCCCTGGGTCCGGTCCTGTGAAGAA
GCATGGCAAGGTTATCATGGGTGCAGTGGCCGATGCCGTTTCAAAAATAGACGACCTTGT
GGGAGGTCTGGCCTCCCTGAGCGAACTTCATGCTTCCAAGCTGCGTGTTGACCCGGCCAA
CTTCAAGATCCTCGCACACAATGTCATCGTGGTCATCGGCATGCTCTTCCCTGGAGACTT
CCCCCCAGAGGTTCACATGTCAGTTGACAAGTTTTTCCAGAAC---TTGGCTCTGGCTCT
CTCTGAGAAGTACCGCTAA通过在序列中插入-来使得序列对齐。如果不习惯命令行的操作方式,也有在线服务可以使用。EBI提供的在线服务网址如下
https://www.ebi.ac.uk/Tools/msa/clustalo/
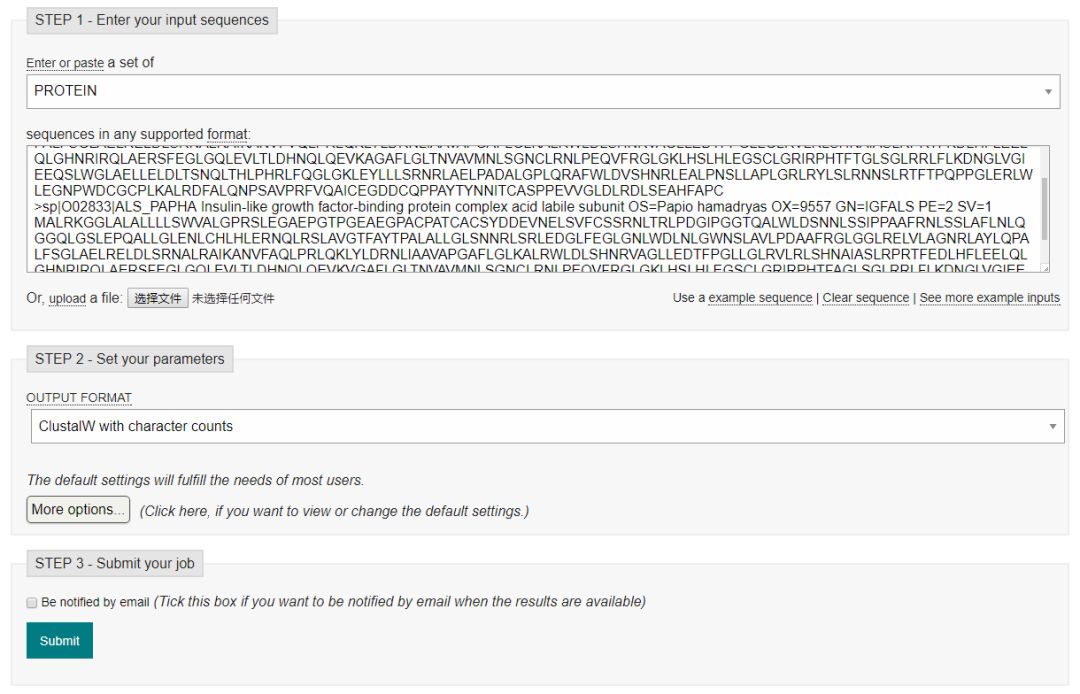
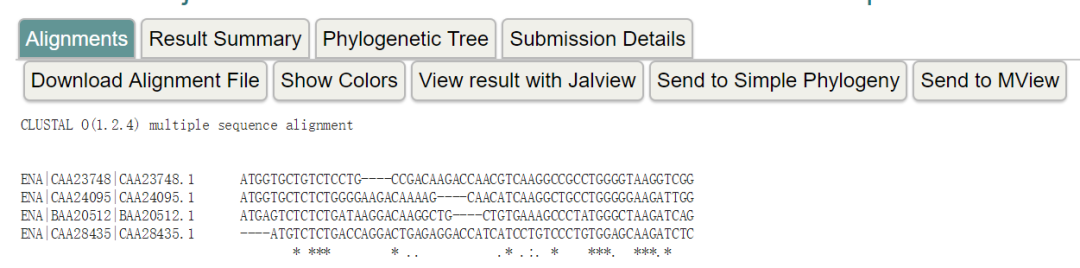
使用非常简单,输入序列,调整参数设置,然后提交即可。在输出结果中,还提供了颜色标记,进化树可视化等功能。
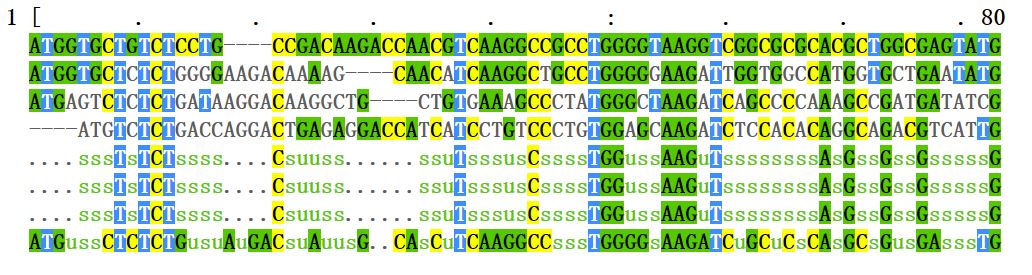
通过Mview可视化多序列比对结果,示意如下
也支持导出到Jalview软件中进行可视化。
通过Phylogenetic Tree可以查看进化树的结果,默认采用NJ法建树,示意如下

也可以通过Send to Simple Phylogeny, 创建进化树,支持NJ和UPGMA两种建树方式。
看完上述内容,你们掌握怎样使用Clustal进行多序列比对的方法了吗?如果还想学到更多技能或想了解更多相关内容,欢迎关注亿速云行业资讯频道,感谢各位的阅读!
亿速云「云服务器」,即开即用、新一代英特尔至强铂金CPU、三副本存储NVMe SSD云盘,价格低至29元/月。点击查看>>
免责声明:本站发布的内容(图片、视频和文字)以原创、转载和分享为主,文章观点不代表本网站立场,如果涉及侵权请联系站长邮箱:is@yisu.com进行举报,并提供相关证据,一经查实,将立刻删除涉嫌侵权内容。
原文链接:https://my.oschina.net/u/4580290/blog/4620797