这期内容当中小编将会给大家带来有关可以做structure的R语言包LEA是怎样的,文章内容丰富且以专业的角度为大家分析和叙述,阅读完这篇文章希望大家可以有所收获。
关于分群的软件,之前写了structure 2.3.4 软件使用指南,软件虽然有windows版本,但是操作太麻烦了,也写了Admixture使用说明文档cookbook,但是只有Linux版本,使用起来有难度。难道不能使用R语言进行structure绘图么?结果来了:LEA!
LEA: An R package for landscape and ecological association studies
使用说明文档
不同格式的数据使用LEA
This short tutorial explains how population structure analyses reproducing the results of the widely-used computer program structure can be performed using commands in the R language. The method works for any operating systems, and it does not require the installation
of structure or additional computer programs. The R program allows running population structure inference algorithms, choosing the number of clusters, and showing admixture coefficient bar-plots using a few commands. The methods used by R are fast and accurate, and they
are free of standard population genetic equilibrium hypotheses. In addition, these methods allow their users to play with a large panel of graphical functions for displaying pie-charts and interpolated admixture coefficients on geographic maps.
划重点:
可以在R语言中实现软件Structure的功能
可以做类似admixture的图
简单操作, 几个命令实现相关功能
C语言开发, 可以处理大数据
install.packages(c("fields","RColorBrewer","mapplots"))
source("http://bioconductor.org/biocLite.R")
biocLite("LEA")如果安装不成功, 也可以通过CRAN把软件包下载到本地, 进行安装:
install.packages("LEA_1.4.0_tar.gz", repos = NULL, type ="source")载入两个函数, 进行格式转化以及可视化:
source("http://membres-timc.imag.fr/Olivier.Francois/Conversion.R")
source("http://membres-timc.imag.fr/Olivier.Francois/POPSutilities.R")plink格式的ped文件, 具体格式参考:plink格式的ped和map文件及转化为012的方法
1 SAMPLE0 0 0 2 2 1 2 3 3 1 1 2 1
2 SAMPLE1 0 0 1 2 2 1 1 3 0 4 1 1
3 SAMPLE2 0 0 2 1 2 2 3 3 1 4 1 1前六列为:
家系ID
个体ID
父本
母本
性别
表型值
SNP1-1(SNP1的第一个位点)
SNP1-2(SNP的第二个位点)
测试数据采用admixture的示例数据, 使用plink将其转化为ped文件
library(LEA)
# 结果会生成test.geno文件的数据.
output = ped2lfmm("test.ped")# 使用LEA进行structure进行分析
library(LEA)
obj.snmf = snmf("test.geno", K = 3, alpha = 100, project = "new")
qmatrix = Q(obj.snmf, K = 3)
head(qmatrix)
barplot(t(qmatrix), col = rainbow(3), border = NA, space = 0,
xlab = "Individuals", ylab = "Admixture coefficients")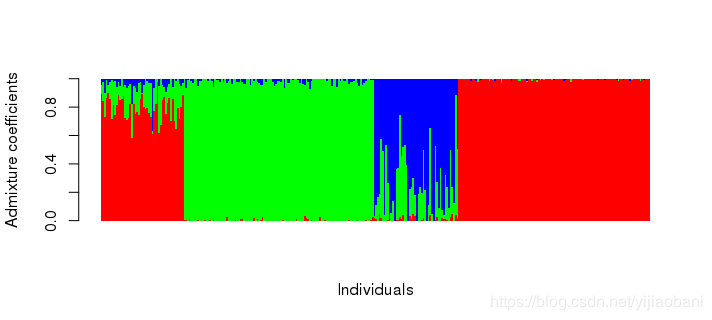
对比admixture的结果
# 对比admixture结果
qad = read.table("test.3.Q")
head(qad)
barplot(t(qad), col = rainbow(3), border = NA, space = 0,
xlab = "Individuals", ylab = "Admixture coefficients")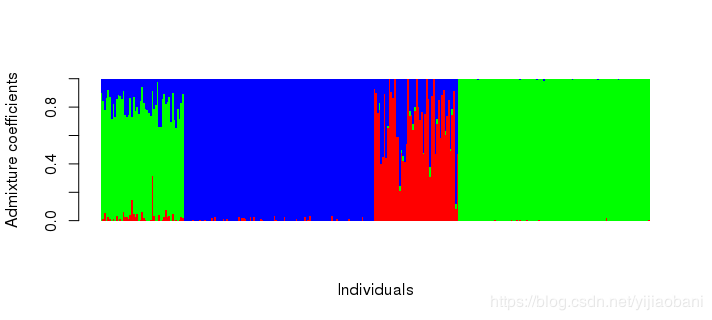
snmf选择最优K值# 绘制折线图, 选择最优K值.
plot(project, col = "blue", pch = 19, cex = 1.2)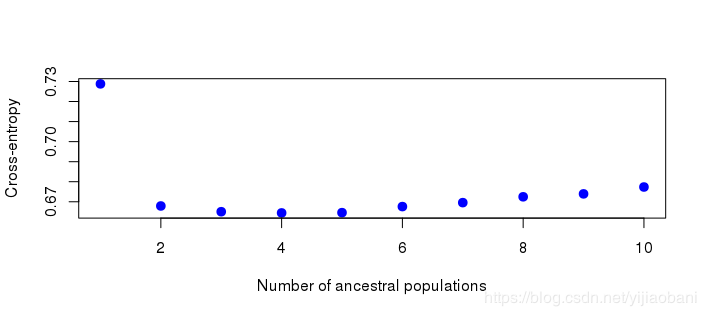
可以看出, K=3时, 最小, 因此选择K=3.
上述就是小编为大家分享的可以做structure的R语言包LEA是怎样的了,如果刚好有类似的疑惑,不妨参照上述分析进行理解。如果想知道更多相关知识,欢迎关注亿速云行业资讯频道。
免责声明:本站发布的内容(图片、视频和文字)以原创、转载和分享为主,文章观点不代表本网站立场,如果涉及侵权请联系站长邮箱:is@yisu.com进行举报,并提供相关证据,一经查实,将立刻删除涉嫌侵权内容。