本篇文章为大家展示了如何使用igvtools可视化测序深度分布,内容简明扼要并且容易理解,绝对能使你眼前一亮,通过这篇文章的详细介绍希望你能有所收获。
igvtools是最常用的NGS数据可视化工具之一,功能非常强大,可以展示序列比对,拷贝数变异,突变位点等多种数据的分布,网址如下
小编主要介绍如何使用这个工具来展示测序深度的分布,对于测序深度,有多种格式的文件都存储了相应的信息,比如我们之前介绍过的bedgraph, bigwig等。igvtools当然支持直接导入这种格式的文件,但是igvtools官方更推荐使用它们自己制定的一种文件格式-TDF。
TDF格式也是采用了滑动窗口的方式,用窗口内的数据的平均值来代表该窗口的结果,最终生成了一个二进制的文件,这个文件igvtools处理起来更加快速。通过igvtools的命令行工具,可以由bam文件生成对应的tdf格式的文件,用法如下
igvtools count \
-z 5 -w 10 -e 0 \
sample.bam \
sample.tdf \
genome.fa生成了tdf格式的文件之后,就可以导入到igvtool之中,首选选择对应的基因组版本,然后通过File->Load from File导入对应的文件。
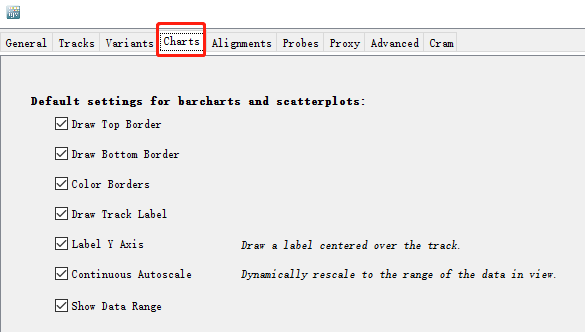
为了展示的更加美观,我们对默认参数进行一些调整。通过View->Preferences按钮, 调整Charts的参数,勾选对应的单选框,示意如下
在igvtools中,每一行展示的数据称之为track, 通过右键弹出的菜单,可以对每个track的颜色,数值范围进行调整。调整参数之后,可以生成如下所示的结果
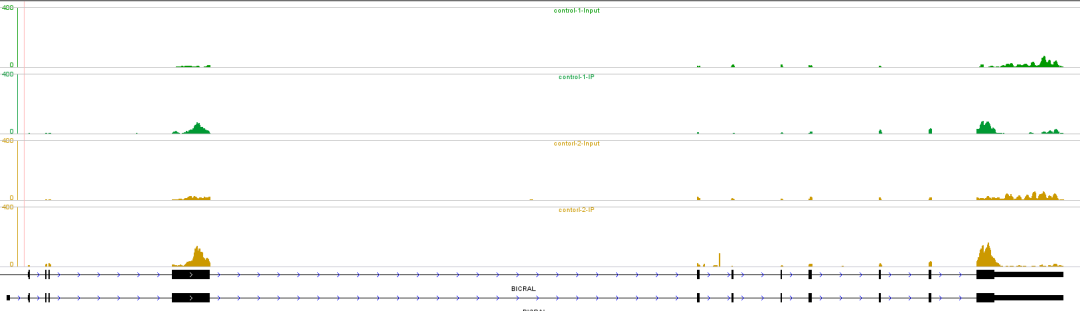
igvtools也支持导出图片,通过File->Save Images可以导出png, svg, jpeg等多种格式的文件。
上述内容就是如何使用igvtools可视化测序深度分布,你们学到知识或技能了吗?如果还想学到更多技能或者丰富自己的知识储备,欢迎关注亿速云行业资讯频道。
免责声明:本站发布的内容(图片、视频和文字)以原创、转载和分享为主,文章观点不代表本网站立场,如果涉及侵权请联系站长邮箱:is@yisu.com进行举报,并提供相关证据,一经查实,将立刻删除涉嫌侵权内容。